Ribonuclease H
| Ribonuclease H | |||||||||
|---|---|---|---|---|---|---|---|---|---|

| |||||||||
| Estrutura cristalográfica da RNase HI de E. coli.[1] | |||||||||
| Identificadores | |||||||||
| Número EC | 3.1.26.4 | ||||||||
| Número CAS | 9050-76-4 | ||||||||
| Bases de datos | |||||||||
| IntEnz | vista de IntEnz | ||||||||
| BRENDA | entrada de BRENDA | ||||||||
| ExPASy | vista de NiceZyme | ||||||||
| KEGG | entrada de KEGG | ||||||||
| MetaCyc | vía metabólica | ||||||||
| PRIAM | perfil | ||||||||
| Estruturas PDB | RCSB PDB PDBe PDBj PDBsum | ||||||||
| Gene Ontology | AmiGO / EGO | ||||||||
| |||||||||
| Ribonuclease H retroviral | |||||||||
|---|---|---|---|---|---|---|---|---|---|
| Identificadores | |||||||||
| Número EC | 3.1.26.13 | ||||||||
| Bases de datos | |||||||||
| IntEnz | vista de IntEnz | ||||||||
| BRENDA | entrada de BRENDA | ||||||||
| ExPASy | vista de NiceZyme | ||||||||
| KEGG | entrada de KEGG | ||||||||
| MetaCyc | vía metabólica | ||||||||
| PRIAM | perfil | ||||||||
| Estruturas PDB | RCSB PDB PDBe PDBj PDBsum | ||||||||
| |||||||||
As ribonucleases H (abreviadas como RNase H ou RNH) forman unha familia de encimas endonucleases non específicos de secuencia que catalizan a clivaxe de ARN nun substrato ARN/ADN por medio dun mecanismo hidrolítico. Os membros da familia da RNase H poden encontrarse en case todos os organismos, desde bacterias a arqueas e a eucariotas.
A familia está dividida en grupos relacionados evolutivamente con preferencias de substrato lixeiramente diferentes, designadas cos nomes xerais de ribonuclease H1 e H2.[2] O xenoma humano codifica tanto a H1 coma a H2. A ribonuclease H2 humana é un complexo heterotrimérico composto de tres subunidades, e as mutacións en cada unha delas están entre as causas xenéticas da rara enfermidade chamada síndrome de Aicardi-Goutières.[3] Un terceiro tipo, estreitamente relacionado con H2, soamente se encontra nuns poucos procariotas,[4] mentres que as H1 e H2 aparecen en todos os dominios da vida.[4] Adicionalmente, os dominios da ribonuclease H retroviral de tipo RNase H1 aparecen en proteínas transcriptase inversa multidominio, que codifican os retrovirus, como o VIH, e cómpren para a replicación viral.[5][6]
En eucariotas, a ribonuclease H1 está implicada na replicación do ADN do xenoma mitocondrial. Tanto a H1 coma a H2 están implicadas en tarefas de mantemento do xenoma, como o procesamento de estruturas en bucle R.[2][7]
Clasificación e nomenclatura
[editar | editar a fonte]A ribonuclease H é unha familia de encimas endonucleases que comparten unha especificidade de substrato polas febras de ARN de dobres hélices ARN-ADN. Por definición, as RNases H clivan o esqueleto de enlaces fosfodiéster do ARN deixando un extremo 3' hidroxilo e un grupo 5' fosfato.[7] As RNases H foron propostas como membros dunha superfamilia relacionada evolutivamente que comprendería outras nucleases e encimas procesadores de ácidos nucleicos, como as integrases retroviraiss, ADN transposases, resolvases de unión de Holliday, proteínas Piwi e Argonauta, varias exonucleases e a proteína espliceosómica Prp8.[8][9]
As RNases H poden, grosso modo, ser divididas en dous subtipos, H1 e H2, aos que por razóns históricas se lles dá numeración en números arábigos en eucariotas e numeración romana en procariotas. Así, a RNase HI de Escherichia coli é un homólogo da RNase H1 de Homo sapiens.[2][7] En E. coli e en moitos outros procariotas, o xene rnhA codifica a HI e o rnhB a HII. Unha terceira clase relacionada, chamada HIII, aparece nunhas poucas bacterias e arqueas, e está estreitamente relacionada cos encimas HII procariotas.[4]
Estrutura
[editar | editar a fonte]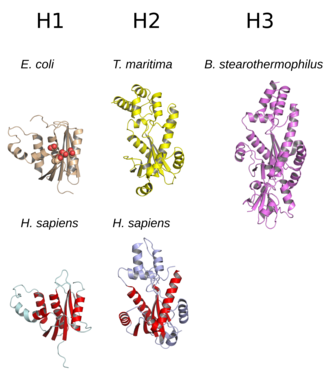
A estrutura da RNase H consiste comunmente nunha folla β de cinco febras rodeada por unha distribución de hélices α.[10] Todas as RNases H teñen un sitio activo centrado nun motivo de secuencia conservado composto por residuos de aspartato e glutamato, a miúdo denominados motivo DEDD. Estes residuos interaccionan con ións magnesio cataliticamente necesarios.[5][7]
As RNases H2 son de maior tamaño que as H1 e xeralmente teñen hélices adicionais. A organización de dominios dos encimas varía; algúns membros eucariotas e procariotas do grupo H1 teñen un pequeno dominio adicional no N-terminal coñecido como "dominio de unión a híbrido", que facilita a unión dos dúplex híbridos ARN:ADN e ás veces confire un incremento de procesividade.[2][7][11] Aínda que todos os membros do grupo H1 e membros procariotas do grupo H2 funcionan como monómeros, os encimas H2 eucariotas son heterotrímeros obrigados.[2][7] Os encimas HIII procariotas son membros do grupo H2 considerado nunn sentido máis amplo e comparten a maioría das características estruturais de H2, coa adición dun dominio de unión á caixa TATA N-terminal.[7] Os dominios de RNase H retroviral que aparecen nas transcriptases inversas multidominio teñen estruturas que lembran estreitamente o grupo H1.[5]
As RNases H1 foron estudadas intensamente para explorar as relacións entre a estrutura e a actividade encimática. Son tamén utilizadas, especialmente o homólogo de E. coli, como sistemas modelos para estudar o pregamento das proteínas.[12][13][14] Dentro do grupo H1, identificouse unha relación entre unha maior afinidade de unión ao substrato e a presenza de elementos estruturais consistentes nunha hélice e bucle flexible, que proporcionan unha superficie de unión ao substrato maior e quimicamente máis básica. A hélice C ten unha distribución taxonómica dispersa; está presente nos homólogos de RNase H1 de E. coli e humanos e ausente no dominio RNase H de VIH, pero hai tamén exemplos de dominios retrovirais con hélices C.[15][16]
Función
[editar | editar a fonte]Os encimas ribonuclease H clivan os enlaces fosfodiéster do ARN dun híbrido bicatenario ARN:ADN, deixando un extemo 3' hidroxilo e un grupo fosfato 5' en ambos os extremos do punto de corte. As RNases H1 e H2 teñen distintas preferencias polo substrato e funcións distintas pero solapadas na célula. En procariotas e eucariotas inferiores, ningún deses encimas é esencial, mentres que se cre que son esenciais nos eucariotas superiores.[2] A actividade combinada dos encimas H1 e H2 está asociada co mantemento da estabilidade xenómica debido á degradación encimática do compoñente ARN de bucle R.[17][18]
Ribonuclease H1
[editar | editar a fonte]| Ribonuclease H | |||||||||
|---|---|---|---|---|---|---|---|---|---|
| Identificadores | |||||||||
| Símbolo | RNase H | ||||||||
| Pfam | PF00075 | ||||||||
| Pfam clan | CL0219 | ||||||||
| InterPro | IPR002156 | ||||||||
| PROSITE | PS50879 | ||||||||
| |||||||||
Os encimas ribonuclease H1 requiren un substrato de polo menos catro pares de bases con ribonucleótidos e non poden eliminar un só ribonucleótido dunha febra que está doutro modo composta de desoxirribonucleótidos. Por esta razón, considérase improbable que as RNases H1 estean implicadas no procesamento dos cebadores de ARN dos fragmentos de Okazaki durante a replicación do ADN.[2] A RNase H1 non é esencial en organismos unicelulares nos que foi investigada; en E. coli, os knockouts para a RNase H1 confiren un fenotipo sensible á temperatura,[7] e en Saccharomyces cerevisiae, producen defectos en resposta ao estrés.[19]
En moitos eucariotas, incluíndo os mamíferos, os xenes da RNase H1 inclúen unha secuencia de destino mitocondrial (MTS, mitochondrial targeting sequence), que causa a expresión de isoformas con e sen secuencia de destino mitocondrial. Como resultado, a RNase H1 está localizada tanto na mitocondria coma no núcleo. Nos modelos de ratos knockout, os mutantes nulos de RNase H1 son letais durante a embrioxénese debido a defectos na replicación do ADN mitocondrial.[2][20][21] Os defectos na replicación do ADN mitocondrial inducidos pola perda de RNase H1 débense probablemente a defectos no procesamento do bucle R.[18]
Ribonuclease H2
[editar | editar a fonte]| Ribonuclease H | |||||||||
|---|---|---|---|---|---|---|---|---|---|
| Identificadores | |||||||||
| Símbolo | RNase HII | ||||||||
| Pfam | PF01351 | ||||||||
| Pfam clan | CL0219 | ||||||||
| InterPro | IPR024567 | ||||||||
| |||||||||
En procariotas, a RNase H2 é encimaticamente activa como proteína monómera. En eucariotas, é un heterodímero obrigado composto dunha subunidade A catalítica e as subunidades B e C estruturais. Mentres que a subunidade A ten grande homoloxía coas RNAase H2 procariotas, e as subunidades B e C non teñen homólogos aparentes en procariotas e están pouco conservadas a nivel de secuencia mesmo entre eucariotas.[22][23] A subunidade B funciona como mediadora das interaccións proteína-proteína entre o complexo H2 e o PCNA, o cal localiza H2 nos focos de replicación.[24]
Tanto os encimas H2 procariotas coma eucariotas poden clivar un só nucleótido nunha febra.[2] porén, teñen patróns de clivaxe e preferencias de substrato lixeiramente diferentes: os encimas procariotas teñen unha procesividade máis baxa e hidrolizan ribonucleótidos sucesivos máis eficazmente que os ribonucleótidos cun desoxirribonucleótido 5', mentres que os encimas eucariotas son máis procesivos e hidrolizan ambos os tipos de substrato con eficacia similar.[2][25] A especificidade de substrato da RNase H2 dálle un papel na reparación por escisión de ribonucleótidos, eliminando os ribonucleótidos incorporados incorrectamente ao ADN, ademais do procesamento do bucle R.[24][26][27] Aínda que no núcleo das células de mamíferos están presentes tanto a H1 coma a H2, a H2 é a fonte dominante de actividade de RNase H alí e é importante para manter a estabilidade xenómica.[24]
Algúns procariotas posúen un xene de tipo H2 adicional denominado RNase HIII na nomenclatura de números romanos usada para os xenes procariotas. As proteinas HIII están máis estreitamente relacionadas co grupo H2 por identidade de secuencia e semellanza estrutural, pero teñen preferencias de substrato que lembran máis claramente a H1.[7][28] A diferenza de HI e HII, que están ambos amplamente espallados entre os procariotas, HIII atópase só nuns poucos organismos cunha distribución taxonómica dispersa; é algo máis común en arqueas e case nunca se atopa no mesmo xenoma procariota que HI.[29]
Mecanismo
[editar | editar a fonte]
O sitio activo de case todas as RNases H contén catro residuos de aminoácidos cargados negativamente, coñecidos como os dominios de motivo DEDD; adoita estar presente a histidina.[2][7]
Os residuos cargados únense a un ou dous ións metálicos que son necesarios para a catálise; baixo condicións fisiolóxicas estes son ións magnesio, pero o manganeso tamén mantén xeralmente a actividade encimática,[2][7] mentres que o calcio pode inhibilo.[11][30] Aínda que os mecanismos catalíticos de dous ións metálicos son moi comúns en encimas implicados na bioquímica do fosfato, debateuse na literatura se se usaban un ou dous ións na catálise da RNase H. En ambos os mecanismos propostos, participa polo menos unha molécula de auga na reacción.[31][32]
A maioría das evidencias experimentais para o mecanismo da catálise da RNase H proceden de medidas realizadas en membros do grupo H1, xeralmente o homólogo de E. coli. Segundo as medidas desta proteína, un dos residuos de aspartato ten un elevado pKa, mentres que outros teñen un pka anormalmente baixo.[33] Non está claro se algún dos residuos do sitio activo participa na reacción como base xeral.[7] Ademais, é posible que un dos átomos de oxíxeno do substrato participe directamente na reacción como unha base.[34]
En bioloxía humana
[editar | editar a fonte]O xenoma humano contén catro xenes que codifican a RNase H:
- RNASEH1, un exemplo do subtipo H1 (monomérico)
- RNASEH2A, unha subunidade catalítica do complexo H2 trimérico
- RNASEH2B, unha subunidade estrutural do complexo H2 trimérico
- RNASEH2C, unha subunidade estrutural do complexo H2 trimérico
Ademais, no xenoma aparece frecuentemente material xenético de orixe retroviral, o que reflicte a integración de xenomas de retrovirus endóxeneos humanos. Ditos eventos de integración teñen como resultado a presenza de xenes codificados pola transcriptase inversa retroviral, o cal inclúe un dominio de RNase H. Un exemplo é ERVK6.[35] Os retrotransposóns de repetición terminal longa son tamén comúns no xenoma humano e a miúdo inclúen os seus propios dominios RNase H, cunha complexa historia evolutiva.[36][37]
Papel en enfermidades
[editar | editar a fonte]
En pequenos estudos, as mutacións na RNase H1 humana foron asociadas coa oftalmoplexia externa progresiva crónica, unha característica común de enfermidade mitocondrial.[21]
As mutacións en calquera das tres subunidades da RNase H2 están ben establecidas como causas dunha rara doenza xenética denominada síndrome de Aicardi–Goutières,[3] a cal se manifesta con síntomas neurolóxicos e dermatolóxicos nunha idade temperá.[39] Os síntomas desta síndrome lembran moito a unha infección conxénita viral e están asociadas coa regulación á alza inapropiada do interferón de tipo I. A síndrome de Aicardi-Goutières pode ser causada igualmente por mutacións noutros xenes: TREX1, SAMHD1, ADAR e MDA5/IFIH1, todos os cales están implicados no procesamento de ácidos nucleicos.[40] A caracterización da distribución mutacional na poboación de pacientes de síndrome de Aicardi-Goutières encontrou un 5% de todas as mutacións nestas síndromes na RNASEH2A, un 36% na 2B, e un 12% na 2C.[41] As mutacións no 2B foron asociadas cun trastorno neurolóxico algo máis suave[42] e cunha ausencia de regulación á alza do xene inducida por interferón, que pode ser detectada en pacientes con outros xenotipos asociados á síndrome de Aicardi-Goutières.[40]
En virus
[editar | editar a fonte]- Véxase tamén: Ribonuclease H retroviral.

Hai dous grupos de virus que usan a transcrición inversa como parte dos seus ciclos vitais: os retrovirus, que codifican os seus xenomas en ARN monocatenario e replícanse por medio dun intermediario de ADN bicatenario; e os virus de ADN bicatenario con transcrición inversa (dsDNA-RT), que replican os seus xenomas de ADN bicatenario por medio dun "prexenoma" intermediario de ARN. Exemplos patóxenos son o virus da inmunodeficiencia humana e o virus da hepatite B, respectivamente. Ambos os dous codifican grandes transcriptases inversas multifuncionais que conteñen dominios RNase H.[44][45]
As transcriptases inversas retrovirais do VIH-1 e o virus da leucemia murina son os membros mellor estudados da familia.[46][47] A transcriptase inversa retroviral é responsable de converter o xenoma de ARN monocatenario do virus en ADN bicatenario. Este proceso require tres pasos: en primeiro lugar, a actividade de ADN polimerase dependente do ARN produce ADN de febra menos (-) a partir do molde de ARN de febra máis (+), xerando un intermediario híbrido ARN:ADN; en segundo lugar, destrúese a febra de ARN; e en terceiro lugar, a actividade de ADN polimerase dependente de ADN sintetiza o ADN de febra máis, xerando ADN bicatenario como o produto final. O segundo paso deste proceso é levado a cabo por un dominio RNase H localizado no C-terminal da transcriptase inversa.[5][6][48][49]
A RNase H realiza tres tipos de accións de clivaxe: a degradación non específica do xenoma de ARN de febra máis, a eliminación específica do cebador de ARNt de febra menos, e a eliminación do cebador do tracto de polipurina rico en purinas da febra máis (PPT).[50] A RNase H intervén tamén no cebado da febra máis, pero non polo método convencional de sintetizar unha secuencia de cebador novo, senón que a RNase H crea un "cebador" a partir do PPT que é resistente á clivaxe da RNase H. Ao eliminar todas as bases agás o PPT, o PPT utilízase como marcador do final da rexión U3 da súa repetición terminal longa.[49]
Como a actividade de RNase H é necesaria para a proliferación viral, este dominio foi considerado unha diana de fármacos para o desenvolvemento de fármacos antirretrovirais usados no tratamento do VIH/SIDA e outras condicións causadas polos retrovirus. Identificáronse os inhibidores da RNase H retroviral de varios quimiotipos diferentes, moitos dos cales teñen un mecanismo de acción baseado na quelación dos catións do sitio activo.[51] Os inhibidores da transcriptase inversa que inhiben especificamente a función polimerase da transcriptase inversa teñen un estendido uso clínico, pero non os inhibidores da función de RNase H; esta é a única función encimática codificada polo VIH que aínda non é diana de fármacos en uso clínico.[48][52]
Evolución
[editar | editar a fonte]As RNases H están amplamente distribuídas e aparecen en todos os dominios da vida. A familia pertence a unha superfamila máis grande de encimas nucleases[8][9] e considérase que é evolutivamente antiga.[53] En xenomas procarióticos están presentes múltiples xenes de RNase H, pero hai pouca correlación entre a presenza de xenes de HI, HII e HIII e as relacións filoxenéticas globais, o que suxire que a transferencia horizontal de xenes puido ter xogado un papel no establecemento da distribución destes encimas entre os seres vivos. As RNases HI e HIII case nunca aparecen no mesmo xenoma procariótico. Cando o xenoma dun organismo contén máis dun xene de RNase H, ás veces teñen diferenzas significativas no nivel de actividade. Suxeriuse que estas observacións reflicten un padrón evolutivo que minimiza a redundancia funcional entre os xenes de RNase H.[7][29] A RNase HIII, que é única dos procariotas, ten unha distribución taxonómica moi espallada e encóntrase en bacterias e arqueas;[29] crese que diverxeu a partir da HII bastante cedo na evolución.[54]
Non está clara a traxectoria evolutiva da RNase H2 en eucariotas, especialmente o mecanismo polo cal os homólogos eucarióticos se converteron en heterotrímeros obrigados. As subunidades B e C non teñen homólogos aparentes en procariotas.[2][23]
Aplicacións
[editar | editar a fonte]Como a RNase H degrada especificamente só o ARN de híbridos bicatenarios de ARN:ADN, é usada comunmente como un reactivo de laboratorio en bioloxía molecular. Disponse comercialmente de preparacións purificadas de RNase HI e HII de E. coli. A RNase HI é utilizada a miúdo para destruír o molde de ARN despois da síntese da primeira febra de ADN complementario (ADNc) por transcrición inversa. Pode tamén utilizarse para clivar secuencias de ARN específicas en presenza de segmentos curtos complementarios de ADN.[55] Para a detección poden utilizarse técnicas de gran sensibilidade como a resonancia plasmónica de superficie.[56][57] A RNase HII pode usarse para degradar o compoñente cebador de ARN dun fragmento de Okazaki ou para introducir amosegas dunha febra en posicións que conteñen un ribonucleótido.[55] Tamén se usa na técnica da reacción en cadea da polimerase (PCR), xa que se describiu unha variante da hot start PCR, chamada PCR dependente de RNase H ou rhPCR, que usa unha RNase HII termoestable procedente da arquea hipertermófila Pyrococcus abyssi.[58] Hai que salientar que a proteína inhibidora da ribonuclease usada habitualmente como reactivo non é efectiva para inhibir a actividade da HI ou da HII.[55]
Historia
[editar | editar a fonte]As ribonucleases H foron descubertas primeiro no laboratorio de Peter Hausen cando os investigadores atoparon a actividade de endonuclease sobre o híbrido de ARN:ADN no timo de tenreira en 1969 e déuselle o nome de "ribonuclease H" para designar a súa especificidade híbrida (H).[22][59][60] A actividade de RNase H foi despois descuberta en E. coli[61] e nunha mostra de oncovirus con xenoma de ARN durante os estudos iniciais sobre a transcrición inversa viral.[62][63] Posteriormente quedou claro que os extractos de timo de tenreira contiñan máis dunha proteína con actividade de RNase H[64] e que E. coli contiña dous xenes de RNase H.[65][66] Orixinalmente, o encima agora coñecido como a RNase H2 en eucariotas foi designado como H1 e viceversa, pero os nomes dos encimas eucariotas foron intercambiados para que se correspondesen cos de E. coli para facilitar as análises comparativas, orixinándose a nomenclatura moderna na cal os encimas procariotas se designan con números romanos e os eucariotas con números arábigos.[2][22][67][68] A RNase HIII procariota, de cuxo descubrimento se informou en 1999, foi o último subtipo de RNase H en ser identificado.[67]
A caracterización da RNase H2 eucariótica foi historicamente todo un reto, en parte pola súa escasa abundancia.[2] Os esforzos coidadosos realizados para purificar o encima suxeriron que o encima eucariota, a diferenza da RNase H de E. coli, tiña moitas subunidades.[69] O homólolgo de Saccharomyces cerevisiae da proteína de E. coli (que é, a subunidade H2A) foi doadamente identificable por bioinformática cando se secuenciou o xenoma do lévedo,[70] pero comprobouse que a proteína correspondente non tiña actividade encimática illada.[2][19] Finalmente, as subunidades B e C de lévedo foron illadas por copurificación e viuse que eran necesarias para a actividade encimática.[71] Porén, as subunidades B e C de lévedos teñen unha identidade de secuencia moi baixa coas súas homólogas doutros organismos, e as proteínas humanas correspondentes foron definitivamente identficadas só despois de que se atoparon mutacións nas tres que causaban a síndrome de Aicardi-Goutières.[2][3]
Notas
[editar | editar a fonte]- ↑ PDB 1JL1; Goedken ER, Marqusee S (December 2001). "Native-state energetics of a thermostabilized variant of ribonuclease HI". Journal of Molecular Biology 314 (4): 863–71. PMID 11734003. doi:10.1006/jmbi.2001.5184.
- ↑ 2,00 2,01 2,02 2,03 2,04 2,05 2,06 2,07 2,08 2,09 2,10 2,11 2,12 2,13 2,14 2,15 2,16 Cerritelli SM, Crouch RJ (March 2009). "Ribonuclease H: the enzymes in eukaryotes". The FEBS Journal 276 (6): 1494–505. PMC 2746905. PMID 19228196. doi:10.1111/j.1742-4658.2009.06908.x.
- ↑ 3,0 3,1 3,2 Crow YJ, Leitch A, Hayward BE, Garner A, Parmar R, Griffith E, et al. (August 2006). "Mutations in genes encoding ribonuclease H2 subunits cause Aicardi-Goutières syndrome and mimic congenital viral brain infection". Nature Genetics 38 (8): 910–6. PMID 16845400. doi:10.1038/ng1842.
- ↑ 4,0 4,1 4,2 Figiel M, Nowotny M (August 2014). "Crystal structure of RNase H3-substrate complex reveals parallel evolution of RNA/DNA hybrid recognition". Nucleic Acids Research 42 (14): 9285–94. PMC 4132731. PMID 25016521. doi:10.1093/nar/gku615.
- ↑ 5,0 5,1 5,2 5,3 Davies JF, Hostomska Z, Hostomsky Z, Jordan SR, Matthews DA (April 1991). "Crystal structure of the ribonuclease H domain of HIV-1 reverse transcriptase". Science 252 (5002): 88–95. PMID 1707186. doi:10.1126/science.1707186.
- ↑ 6,0 6,1 Hansen J, Schulze T, Mellert W, Moelling K (January 1988). "Identification and characterization of HIV-specific RNase H by monoclonal antibody". The EMBO Journal 7 (1): 239–43. PMC 454263. PMID 2452083.
- ↑ 7,00 7,01 7,02 7,03 7,04 7,05 7,06 7,07 7,08 7,09 7,10 7,11 7,12 Tadokoro T, Kanaya S (March 2009). "Ribonuclease H: molecular diversities, substrate binding domains, and catalytic mechanism of the prokaryotic enzymes". The FEBS Journal 276 (6): 1482–93. PMID 19228197. doi:10.1111/j.1742-4658.2009.06907.x.
- ↑ 8,0 8,1 Majorek KA, Dunin-Horkawicz S, Steczkiewicz K, Muszewska A, Nowotny M, Ginalski K, Bujnicki JM (April 2014). "The RNase H-like superfamily: new members, comparative structural analysis and evolutionary classification". Nucleic Acids Research 42 (7): 4160–79. PMC 3985635. PMID 24464998. doi:10.1093/nar/gkt1414.
- ↑ 9,0 9,1 Rice, P.; Craigie, R.; Davies, D. R. (1996-02-01). "Retroviral integrases and their cousins". Current Opinion in Structural Biology 6 (1): 76–83. ISSN 0959-440X. PMID 8696976. doi:10.1016/s0959-440x(96)80098-4.
- ↑ Schmitt TJ, Clark JE, Knotts TA (December 2009). "Thermal and mechanical multistate folding of ribonuclease H". The Journal of Chemical Physics 131 (23): 235101. PMID 20025349. doi:10.1063/1.3270167.
- ↑ 11,0 11,1 Nowotny M, Cerritelli SM, Ghirlando R, Gaidamakov SA, Crouch RJ, Yang W (April 2008). "Specific recognition of RNA/DNA hybrid and enhancement of human RNase H1 activity by HBD". The EMBO Journal 27 (7): 1172–81. PMC 2323259. PMID 18337749. doi:10.1038/emboj.2008.44.
- ↑ Cecconi, Ciro; Shank, Elizabeth A.; Bustamante, Carlos; Marqusee, Susan (2005-09-23). "Direct Observation of the Three-State Folding of a Single Protein Molecule". Science (en inglés) 309 (5743): 2057–2060. ISSN 0036-8075. PMID 16179479. doi:10.1126/science.1116702. Arquivado dende o orixinal o 01 de decembro de 2018. Consultado o 30 de novembro de 2018.
- ↑ Hollien, Julie; Marqusee, Susan (1999-03-01). "A Thermodynamic Comparison of Mesophilic and Thermophilic Ribonucleases H". Biochemistry 38 (12): 3831–3836. ISSN 0006-2960. doi:10.1021/bi982684h.
- ↑ Raschke, Tanya M.; Marqusee, Susan (1997-04-01). "The kinetic folding intermediate of ribonuclease H resembles the acid molten globule and partially unfolded molecules detected under native conditions". Nature Structural & Molecular Biology (en inglés) 4 (4): 298–304. doi:10.1038/nsb0497-298.
- ↑ Schultz SJ, Champoux JJ (June 2008). "RNase H activity: structure, specificity, and function in reverse transcription". Virus Research 134 (1–2): 86–103. PMC 2464458. PMID 18261820. doi:10.1016/j.virusres.2007.12.007.
- ↑ Champoux, James J.; Schultz, Sharon J. (2009-03-01). "Ribonuclease H: properties, substrate specificity and roles in retroviral reverse transcription". FEBS Journal (en inglés) 276 (6): 1506–1516. ISSN 1742-4658. PMC 2742777. PMID 19228195. doi:10.1111/j.1742-4658.2009.06909.x.
- ↑ Amon JD, Koshland D (December 2016). "RNase H enables efficient repair of R-loop induced DNA damage". eLife 5: e20533. PMC 5215079. PMID 27938663. doi:10.7554/eLife.20533.
- ↑ 18,0 18,1 Lima WF, Murray HM, Damle SS, Hart CE, Hung G, De Hoyos CL, Liang XH, Crooke ST (June 2016). "Viable RNaseH1 knockout mice show RNaseH1 is essential for R loop processing, mitochondrial and liver function". Nucleic Acids Research 44 (11): 5299–312. PMC 4914116. PMID 27131367. doi:10.1093/nar/gkw350.
- ↑ 19,0 19,1 Arudchandran A, Cerritelli S, Narimatsu S, Itaya M, Shin DY, Shimada Y, Crouch RJ (2000). "The absence of ribonuclease H1 or H2 alters the sensitivity of Saccharomyces cerevisiae to hydroxyurea, caffeine and ethyl methanesulphonate: implications for roles of RNases H in DNA replication and repair". Genes to Cells 5 (10): 789–802. PMID 11029655. doi:10.1046/j.1365-2443.2000.00373.x.
- ↑ Cerritelli SM, Frolova EG, Feng C, Grinberg A, Love PE, Crouch RJ (2003). "Failure to produce mitochondrial DNA results in embryonic lethality in Rnaseh1 null mice". Molecular Cell 11 (3): 807–15. PMID 12667461. doi:10.1016/s1097-2765(03)00088-1.
- ↑ 21,0 21,1 Reyes A, Melchionda L, Nasca A, Carrara F, Lamantea E, Zanolini A, Lamperti C, Fang M, Zhang J, Ronchi D, Bonato S, Fagiolari G, Moggio M, Ghezzi D, Zeviani M (July 2015). "RNASEH1 Mutations Impair mtDNA Replication and Cause Adult-Onset Mitochondrial Encephalomyopathy". American Journal of Human Genetics 97 (1): 186–93. PMC 4572567. PMID 26094573. doi:10.1016/j.ajhg.2015.05.013.
- ↑ 22,0 22,1 22,2 Hollis T, Shaban NM (2011-01-01). Nicholson AW, ed. Ribonucleases. Nucleic Acids and Molecular Biology. Springer Berlin Heidelberg. pp. 299–317. ISBN 9783642210778. doi:10.1007/978-3-642-21078-5_12.
- ↑ 23,0 23,1 Chon H, Vassilev A, DePamphilis ML, Zhao Y, Zhang J, Burgers PM, Crouch RJ, Cerritelli SM (January 2009). "Contributions of the two accessory subunits, RNASEH2B and RNASEH2C, to the activity and properties of the human RNase H2 complex". Nucleic Acids Research 37 (1): 96–110. PMC 2615623. PMID 19015152. doi:10.1093/nar/gkn913.
- ↑ 24,0 24,1 24,2 Reijns MA, Jackson AP (August 2014). "Ribonuclease H2 in health and disease". Biochemical Society Transactions 42 (4): 717–25. PMID 25109948. doi:10.1042/BST20140079.
- ↑ Chon H, Vassilev A, DePamphilis ML, Zhao Y, Zhang J, Burgers PM, Crouch RJ, Cerritelli SM (January 2009). "Contributions of the two accessory subunits, RNASEH2B and RNASEH2C, to the activity and properties of the human RNase H2 complex". Nucleic Acids Research (en inglés) 37 (1): 96–110. PMC 2615623. PMID 19015152. doi:10.1093/nar/gkn913.
- ↑ Wahba L, Amon JD, Koshland D, Vuica-Ross M (December 2011). "RNase H and multiple RNA biogenesis factors cooperate to prevent RNA:DNA hybrids from generating genome instability". Molecular Cell 44 (6): 978–88. PMC 3271842. PMID 22195970. doi:10.1016/j.molcel.2011.10.017.
- ↑ Kim N, Huang SN, Williams JS, Li YC, Clark AB, Cho JE, Kunkel TA, Pommier Y, Jinks-Robertson S (June 2011). "Mutagenic processing of ribonucleotides in DNA by yeast topoisomerase I". Science 332 (6037): 1561–4. PMC 3380281. PMID 21700875. doi:10.1126/science.1205016.
- ↑ Ohtani N, Haruki M, Morikawa M, Crouch RJ, Itaya M, Kanaya S (January 1999). "Identification of the genes encoding Mn2+-dependent RNase HII and Mg2+-dependent RNase HIII from Bacillus subtilis: classification of RNases H into three families". Biochemistry 38 (2): 605–18. PMID 9888800. doi:10.1021/bi982207z.
- ↑ 29,0 29,1 29,2 Kochiwa H, Tomita M, Kanai A (July 2007). "Evolution of ribonuclease H genes in prokaryotes to avoid inheritance of redundant genes". BMC Evolutionary Biology 7: 128. PMC 1950709. PMID 17663799. doi:10.1186/1471-2148-7-128.
- ↑ Rosta E, Yang W, Hummer G (February 2014). "Calcium inhibition of ribonuclease H1 two-metal ion catalysis". Journal of the American Chemical Society 136 (8): 3137–44. PMC 3985467. PMID 24499076. doi:10.1021/ja411408x.
- ↑ Klumpp K, Hang JQ, Rajendran S, Yang Y, Derosier A, Wong Kai In P, Overton H, Parkes KE, Cammack N, Martin JA (December 2003). "Two-metal ion mechanism of RNA cleavage by HIV RNase H and mechanism-based design of selective HIV RNase H inhibitors". Nucleic Acids Research 31 (23): 6852–9. PMC 290251. PMID 14627818. doi:10.1093/nar/gkg881.
- ↑ Yang W, Lee JY, Nowotny M (April 2006). "Making and breaking nucleic acids: two-Mg2+-ion catalysis and substrate specificity". Molecular Cell 22 (1): 5–13. PMID 16600865. doi:10.1016/j.molcel.2006.03.013.
- ↑ Oda, Yasushi; Yamazaki, Toshio; Nagayama, Kuniaki; Kanaya, Shigenori; Kuroda, Yutaka; Nakamura, Haruki (1994-05-01). "Individual Ionization Constants of All the Carboxyl Groups in Ribonuclease HI from Escherichia coli Determined by NMR". Biochemistry 33 (17): 5275–5284. ISSN 0006-2960. doi:10.1021/bi00183a034.
- ↑ De Vivo, Marco; Dal Peraro, Matteo; Klein, Michael L. (2008-08-01). "Phosphodiester Cleavage in Ribonuclease H Occurs via an Associative Two-Metal-Aided Catalytic Mechanism". Journal of the American Chemical Society 130 (33): 10955–10962. ISSN 0002-7863. PMC 2745632. PMID 18662000. doi:10.1021/ja8005786.
- ↑ Reus K, Mayer J, Sauter M, Scherer D, Müller-Lantzsch N, Meese E (March 2001). "Genomic organization of the human endogenous retrovirus HERV-K(HML-2.HOM) (ERVK6) on chromosome 7". Genomics 72 (3): 314–20. PMID 11401447. doi:10.1006/geno.2000.6488.
- ↑ Ustyantsev K, Novikova O, Blinov A, Smyshlyaev G (May 2015). "Convergent evolution of ribonuclease h in LTR retrotransposons and retroviruses". Molecular Biology and Evolution 32 (5): 1197–207. PMC 4408406. PMID 25605791. doi:10.1093/molbev/msv008.
- ↑ Malik HS. "Ribonuclease H evolution in retrotransposable elements". Cytogenetic and Genome Research 110 (1–4): 392–401. PMID 16093691. doi:10.1159/000084971.
- ↑ Figiel M, Chon H, Cerritelli SM, Cybulska M, Crouch RJ, Nowotny M (March 2011). "The structural and biochemical characterization of human RNase H2 complex reveals the molecular basis for substrate recognition and Aicardi-Goutières syndrome defects". The Journal of Biological Chemistry 286 (12): 10540–50. PMC 3060507. PMID 21177858. doi:10.1074/jbc.M110.181974.
- ↑ Orcesi S, La Piana R, Fazzi E (2009). "Aicardi-Goutieres syndrome". British Medical Bulletin 89: 183–201. PMID 19129251. doi:10.1093/bmb/ldn049.
- ↑ 40,0 40,1 Crow YJ, Manel N (July 2015). "Aicardi-Goutières syndrome and the type I interferonopathies". Nature Reviews. Immunology 15 (7): 429–40. PMID 26052098. doi:10.1038/nri3850.
- ↑ Crow YJ, Chase DS, Lowenstein Schmidt J, Szynkiewicz M, Forte GM, Gornall HL, et al. (February 2015). "Characterization of human disease phenotypes associated with mutations in TREX1, RNASEH2A, RNASEH2B, RNASEH2C, SAMHD1, ADAR, and IFIH1". American Journal of Medical Genetics. Part A 167A (2): 296–312. PMC 4382202. PMID 25604658. doi:10.1002/ajmg.a.36887.
- ↑ Rice G, Patrick T, Parmar R, Taylor CF, Aeby A, Aicardi J, et al. (October 2007). "Clinical and molecular phenotype of Aicardi-Goutieres syndrome". American Journal of Human Genetics 81 (4): 713–25. PMC 2227922. PMID 17846997. doi:10.1086/521373.
- ↑ Sarafianos, S. G.; Das, K.; Tantillo, C.; Clark, A. D.; Ding, J.; Whitcomb, J. M.; Boyer, P. L.; Hughes, S. H.; Arnold, E. (2001-03-15). "Crystal structure of HIV-1 reverse transcriptase in complex with a polypurine tract RNA:DNA". The EMBO Journal 20 (6): 1449–1461. ISSN 0261-4189. PMC 145536. PMID 11250910. doi:10.1093/emboj/20.6.1449.
- ↑ Seeger, Christoph; Mason, William S. "Molecular biology of hepatitis B virus infection". Virology. 479–480: 672–686. PMC 4424072. PMID 25759099. doi:10.1016/j.virol.2015.02.031.
- ↑ Moelling, Karin; Broecker, Felix; Kerrigan, JohnE. (2014-01-01). Vicenzi, Elisa; Poli, Guido, eds. Human Retroviruses. Methods in Molecular Biology (en English). Humana Press. pp. 71–84. ISBN 9781627036696. doi:10.1007/978-1-62703-670-2_7.
- ↑ Mizuno M, Yasukawa K, Inouye K (February 2010). "Insight into the mechanism of the stabilization of moloney murine leukaemia virus reverse transcriptase by eliminating RNase H activity". Bioscience, Biotechnology, and Biochemistry 74 (2): 440–2. PMID 20139597. doi:10.1271/bbb.90777.
- ↑ Coté ML, Roth MJ (June 2008). "Murine leukemia virus reverse transcriptase: structural comparison with HIV-1 reverse transcriptase". Virus Research 134 (1–2): 186–202. PMC 2443788. PMID 18294720. doi:10.1016/j.virusres.2008.01.001.
- ↑ 48,0 48,1 Nowotny, Marcin; Figiel, Małgorzata (2013-01-01). LeGrice, Stuart; Gotte, Matthias, eds. Human Immunodeficiency Virus Reverse Transcriptase (en inglés). Springer New York. pp. 53–75. ISBN 9781461472902. doi:10.1007/978-1-4614-7291-9_3.
- ↑ 49,0 49,1 Beilhartz GL, Götte M (April 2010). "HIV-1 Ribonuclease H: Structure, Catalytic Mechanism and Inhibitors". Viruses 2 (4): 900–26. PMC 3185654. PMID 21994660. doi:10.3390/v2040900.
- ↑ Klarmann GJ, Hawkins ME, Le Grice SF (2002). "Uncovering the complexities of retroviral ribonuclease H reveals its potential as a therapeutic target". AIDS Reviews 4 (4): 183–94. PMID 12555693.
- ↑ Tramontano, E.; Santo, R. Di. "HIV-1 RT-Associated RNase H Function Inhibitors: Recent Advances in Drug Development". Current Medicinal Chemistry (en inglés) 17 (26): 2837–2853. doi:10.2174/092986710792065045.
- ↑ Cao, Lili; Song, Weiguo; De Clercq, Erik; Zhan, Peng; Liu, Xinyong (2014-06-01). "Recent progress in the research of small molecule HIV-1 RNase H inhibitors". Current Medicinal Chemistry 21 (17): 1956–1967. ISSN 1875-533X. PMID 24438523. doi:10.2174/0929867321666140120121158.
- ↑ Ma, Bin-Guang; Chen, Lei; Ji, Hong-Fang; Chen, Zhong-Hua; Yang, Fu-Rong; Wang, Ling; Qu, Ge; Jiang, Ying-Ying; Ji, Cong (2008-02-15). "Characters of very ancient proteins". Biochemical and Biophysical Research Communications 366 (3): 607–611. doi:10.1016/j.bbrc.2007.12.014.
- ↑ Brindefalk, Björn; Dessailly, Benoit H.; Yeats, Corin; Orengo, Christine; Werner, Finn; Poole, Anthony M. (2013-03-01). "Evolutionary history of the TBP-domain superfamily". Nucleic Acids Research 41 (5): 2832–2845. ISSN 0305-1048. PMC 3597702. PMID 23376926. doi:10.1093/nar/gkt045.
- ↑ 55,0 55,1 55,2 Nichols, Nicole M.; Yue, Dongxian (2001-01-01). Current Protocols in Molecular Biology (en inglés). John Wiley & Sons, Inc. ISBN 9780471142720. doi:10.1002/0471142727.mb0313s84.
- ↑ Loo JF, Wang SS, Peng F, He JA, He L, Guo YC, Gu DY, Kwok HC, Wu SY, Ho HP, Xie WD, Shao YH, Kong SK (July 2015). "A non-PCR SPR platform using RNase H to detect MicroRNA 29a-3p from throat swabs of human subjects with influenza A virus H1N1 infection". The Analyst 140 (13): 4566–75. PMID 26000345. doi:10.1039/C5AN00679A.
- ↑ Goodrich TT, Lee HJ, Corn RM (April 2004). "Direct detection of genomic DNA by enzymatically amplified SPR imaging measurements of RNA microarrays". Journal of the American Chemical Society 126 (13): 4086–7. PMID 15053580. doi:10.1021/ja039823p.
- ↑ Dobosy JR, Rose SD, Beltz KR, Rupp SM, Powers KM, Behlke MA, Walder JA (August 2011). "RNase H-dependent PCR (rhPCR): improved specificity and single nucleotide polymorphism detection using blocked cleavable primers". BMC Biotechnology 11: 80. PMC 3224242. PMID 21831278. doi:10.1186/1472-6750-11-80.
- ↑ Stein, Hans; Hausen, Peter (1969-10-17). "Enzyme from Calf Thymus Degrading the RNA Moiety of DNA-RNA Hybrids: Effect on DNA-Dependent RNA Polymerase". Science (en inglés) 166 (3903): 393–395. ISSN 0036-8075. PMID 5812039. doi:10.1126/science.166.3903.393. Arquivado dende o orixinal o 02 de decembro de 2018. Consultado o 30 de novembro de 2018.
- ↑ Hausen, Peter; Stein, Hans (1970-06-01). "Ribonuclease H". European Journal of Biochemistry (en inglés) 14 (2): 278–283. ISSN 1432-1033. doi:10.1111/j.1432-1033.1970.tb00287.x.
- ↑ Miller, H. I.; Riggs, A. D.; Gill, G. N. (1973-04-10). "Ribonuclease H (hybrid) in Escherichia coli. Identification and characterization". The Journal of Biological Chemistry 248 (7): 2621–2624. ISSN 0021-9258. PMID 4572736.
- ↑ Mölling, K.; Bolognesi, D. P.; Bauer, H.; Büsen, W.; Plassmann, H. W.; Hausen, P. (1971-12-22). "Association of viral reverse transcriptase with an enzyme degrading the RNA moiety of RNA-DNA hybrids". Nature New Biology 234 (51): 240–243. ISSN 0090-0028. PMID 4331605. doi:10.1038/newbio234240a0.
- ↑ Grandgenett, D. P.; Gerard, G. F.; Green, M. (1972-12-01). "Ribonuclease H: a ubiquitous activity in virions of ribonucleic acid tumor viruses". Journal of Virology 10 (6): 1136–1142. ISSN 0022-538X. PMC 356594. PMID 4118867.
- ↑ Büsen, Werner; Hausen, Peter (1975-03-01). "Distinct Ribonuclease H Activities in Calf Thymus". European Journal of Biochemistry (en inglés) 52 (1): 179–190. ISSN 1432-1033. doi:10.1111/j.1432-1033.1975.tb03985.x.
- ↑ Kanaya, S.; Crouch, R. J. (1983-01-25). "DNA sequence of the gene coding for Escherichia coli ribonuclease H". The Journal of Biological Chemistry 258 (2): 1276–1281. ISSN 0021-9258. PMID 6296074.
- ↑ Itaya, M. (1990-11-01). "Isolation and characterization of a second RNase H (RNase HII) of Escherichia coli K-12 encoded by the rnhB gene". Proceedings of the National Academy of Sciences of the United States of America 87 (21): 8587–8591. ISSN 0027-8424. PMC 55002. PMID 2172991. doi:10.1073/pnas.87.21.8587.
- ↑ 67,0 67,1 Ohtani, N.; Haruki, M.; Morikawa, M.; Crouch, R. J.; Itaya, M.; Kanaya, S. (1999-01-12). "Identification of the genes encoding Mn2+-dependent RNase HII and Mg2+-dependent RNase HIII from Bacillus subtilis: classification of RNases H into three families". Biochemistry 38 (2): 605–618. ISSN 0006-2960. PMID 9888800. doi:10.1021/bi982207z.
- ↑ Crouch, R. J.; Arudchandran, A.; Cerritelli, S. M. (2001-01-01). "RNase H1 of Saccharomyces cerevisiae: methods and nomenclature". Methods in Enzymology 341: 395–413. ISSN 0076-6879. PMID 11582793. doi:10.1016/s0076-6879(01)41166-9.
- ↑ Frank, P.; Braunshofer-Reiter, C.; Wintersberger, U.; Grimm, R.; Büsen, W. (1998-10-27). "Cloning of the cDNA encoding the large subunit of human RNase HI, a homologue of the prokaryotic RNase HII". Proceedings of the National Academy of Sciences of the United States of America 95 (22): 12872–12877. ISSN 0027-8424. PMC 23637. PMID 9789007. doi:10.1073/pnas.95.22.12872.
- ↑ Frank, P.; Braunshofer-Reiter, C.; Wintersberger, U. (1998-01-02). "Yeast RNase H(35) is the counterpart of the mammalian RNase HI, and is evolutionarily related to prokaryotic RNase HII". FEBS Letters 421 (1): 23–26. ISSN 0014-5793. PMID 9462832. doi:10.1016/s0014-5793(97)01528-7.
- ↑ Jeong, Ho-Sang; Backlund, Peter S.; Chen, Hao-Chia; Karavanov, Alexander A.; Crouch, Robert J. (2004-01-01). "RNase H2 of Saccharomyces cerevisiae is a complex of three proteins". Nucleic Acids Research 32 (2): 407–414. ISSN 1362-4962. PMC 373335. PMID 14734815. doi:10.1093/nar/gkh209.
Véxase tamén
[editar | editar a fonte]Ligazóns externas
[editar | editar a fonte]- GeneReviews/NCBI/NIH/UW entrada en síndrome de Aicardi-Goutières
- RNase H Medical Subject Headings (MeSH) na Biblioteca Nacional de Medicina dos EUA.